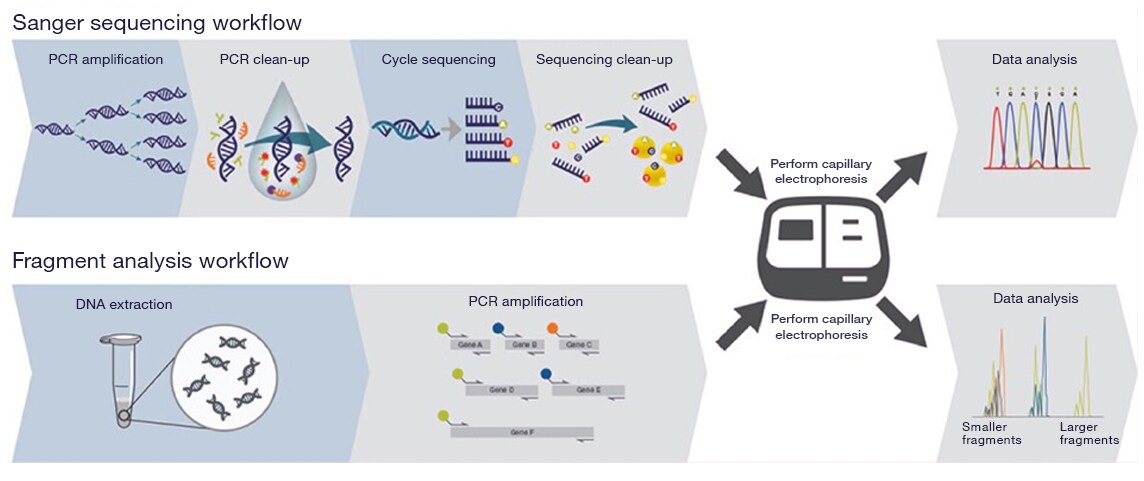
Plasmid Sequencing
Accurately analyze subcloned inserts with read lengths ranging from <300 bp to >600 bp.
Species Identification
Identify bacterial 16s rRNA with access to the groundbreaking phylogenetic research work of Carl Woese et al.
CRISPR-Cas9 Gene Editing
Evaluate the efficiency of CRISPR events, quantify gene editing activity (target region analyzed using TIDE software), characterize the gene target in cell lines, assess gene copy number, and more.
Cell Line Authentication (CLA)
Confidently detect contaminating cell lines with sensitivity and accuracy.
SNP Genotyping
The Applied Biosystems™ SNaPshot™ Multiplex System saves time with built-in reporting of fragment analysis and by combining sequencing and fragment analysis on the same plate during the same run.
MLPA
Analyze human copy number variation (CNV) with Multiplex Ligation-Dependent Probe Amplification (MLPA™).
Oncology Research
Confirm next-generation sequencing.